Introducción
Los begomovirus, pertenecientes a la familia Geminiviridae, son virus de plantas que contienen DNA circular de cadena sencilla con uno (monopartito) o dos (bipartito) DNA-A y DNA-B) componentes genómicos. Son transmitidos por la mosca blanca (Bemisia tabaci ) y actualmente son responsables de muchas enfermedades emergentes en cultivos agronómicos (Zerbini et al., 2017).
En las últimas dos décadas la presencia de begomovirus se ha incrementado notablemente convirtiéndose en un problema emergente debido a las mutaciones y recombinaciones genéticas que han sido identificadas (Lefeuvre y Moriones, 2015; Seal et al., 2006). Este incremento está asociado con la presencia de su principal vector (B. tabaci ), un organismo con amplio rango de hospederos, alta capacidad de proliferación, resistencia a varios tipos de insecticidas y con capacidad de dispersión a través de varios pisos climáticos (Ambrozevicius, Calegario, Fontes, Carvalho, y Zerbini, 2002; da Silva et al., 2011; Gaur, Hohn, y Sharma, 2014; Navas-Castillo, Fiallo-Olivé, y Sánchez-Campos, 2011).
En Colombia se registra la presencia de begomovirus en cultivos de tomate localizados en los departamentos de Santander, Cundinamarca y Valle del Cauca, en sitios por encima de 1500 m.s.n.m. (Vaca-Vaca, Betancur-Pérez, y López-López, 2012). La conquista de nuevos nichos y adaptación a pisos altitudinales distintos, posiblemente es debido al cambio climático, en donde, de alguna manera, la mosca blanca cumple un papel fundamental, ya que logra afectar nuevos reservorios, como las arvenses, dando lugar a la ocurrencia de procesos de intercambio genético que favorecen la persistencia y propagación tanto de los begomovirus como de su insecto vector (Duffus, 1971; Marwal, Prajapat, y Gaur, 2014; Barreto, Hallwass, Aquino, y Inoue-Nagata, 2013).
Hasta la fecha se han reportado en GenBank 47 especies de begomovirus en arvenses. En Colombia se ha detectado la presencia en Momordica charanda (Cucurbitaceae), Rivina humilis (Phyto-laccaceae), Laportea estuans (Urticaceae), Amaranthus dubius (Amaranthaceae), Lantana cámara (Verbenaceae) (López-López, Otavo-Fiscal, y Vaca-Vaca, 2012; López-López, Jara-Tejada, y Vaca-Vaca, 2014) y Croton hirtus (Euphorbiaceae) (Vaca-Vaca, Jara-Tejada, y López-López, 2018).
Por lo anterior, existe la necesidad urgente de obtener información adicional sobre la diversidad y distribución de arvenses asociadas con begomovirus en otros cultivos de importancia agronómica, entre ellos el ají (Capsicum spp.), que probablemente sirven de reservorios de virus. Teniendo en cuenta que Colombia es un país megadiverso, es posible que la diversidad de estos esté asociada con plantas acompañantes, lo que resulta importante para conocer las interacciones entre los virus y cómo las presiones de selección moldean su epidemiologia para extenderse a cultivos de interés económico. De acuerdo con lo anterior, el objetivo de esta investigación fue identificar nuevos hospederos alternos de begomovirus en arvenses asociadas con el cultivo de ají en el Valle del Cauca, Colombia.
Materiales y métodos
Recolección de arvenses
Para el estudio fueron recolectadas hojas jóvenes de arvenses asociadas con el cultivo de ají, en los municipios de Zarzal, Vijes, Toro, Unión, Roldanillo y Guacarí. Las plantas presentaban los síntomas típicos de infección por begomovirus, consistentes en mosaicos amarillos, epinastias, clorosis foliar, abultamientos foliares, enanismo, retraso en el crecimiento y hojas asintomáticas (López López, et al., 2014).
Para la identificación taxonómica de las arvenses se utilizaron las claves de Gentry (1996), Mendoza-Cifuentes y Ramírez-Padilla (2004), además de la colaboración especial del Herbario Josep Cuatrecasas Arumí en la sede de la Universidad Nacional de Colombia, Palmira.
Extracción y calidad de DNA genómico total
Las pruebas moleculares se hicieron en muestras de 80 mg de material foliar de las arvenses recolectadas a partir de las cuales se extrajo el DNA vegetal utilizando Invisorb spin plant mini kit®. Para evaluar la calidad y concentración de DNA vegetal obtenido se realizaron geles de agarosa al 0.8% para DNA y 1% para productos de PCR, siguiendo los protocolos reportados por Sambrook y Russell (2001). La visualización del DNA teñido con bromuro de etilo se hizo con transiluminador Molecular Imagen® GelDocTM XR+ and ChemiDocTM XRS System (BioRad Hércules, CA, USA) y analizados con el software Quanty One 4.6.5. Para estimar el tamaño del DNA se usó el marcador de peso molecular 1 kb Plus DNA Ladder (ThermoFisherScientific®).
Detección de begomovirus por reacción en cadena de la polimerasa (PCR)
La detección de begomovirus se realizó mediante la técnica de PCR (polimerasa chain reaction) utilizando el juego de primers MP82 y MP16 que amplifican un fragmento del gen AR1 (cubierta de proteína) del componente A con un tamaño aproximado de 400 a 600pb (Umaharan, et al., 1998).
Resultados y discusión
Detección de begomovirus en las arvenses recolectadas
En total fueron recolectadas muestras de 179 arvenses (Tabla 1). De cada una de ellas se hizo una extracción de DNA total, de buena calidad y una concentración de 80 ng/ul, aproximadamente. Para evaluar la presencia de begomovirus, se realizó una PCR utilizando los primers descritos por Umaharan, et al., (1998), donde 13 muestras resultaron positivas entre las 179 arvenses colectadas. Las muestras amplificaron un fragmento del gen AR1 con un tamaño aproximado de 400pb (Figura 1).
Tabla 1 Municipios de muestreo de arvenses como posibles hospederos de begomovirus, Valle del Cauca, Colombia.
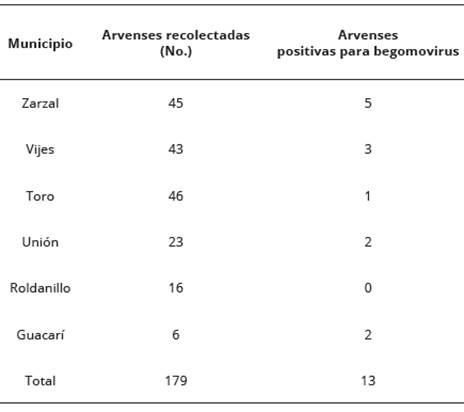

Figura 1 Amplificación viral por PCR de un fragmento de 400pb que comprende desde la región nonanucleotida conservada hasta el gen AR1 del genoma A de begomovirus. Gel de agarosa al 1% teñido con bromuro de etidio. 1, Sida acuta (Z2); 2, Malvastrum sp. (Z14); 3, Malvastrum sp. (Z16); 4, Rivina humilis (Z17); 5, Acalypha sp (Z19.); 6, Phaseolus vulgaris (V58); 7, Parthenium hysterophorus (V60); 8, No identificada (V62); 9, Euphorbia hirta (T119); 10, Rhynchosia minima (U137);11, No identificada (U157); 12, Rhynchosia minima (G177); 13, Euphorbia heterophyla (G181); (-); Control Negativo; (+), Control positivo; M, marcador de peso molecular Gene Ruler 1 kb DNA Ladder Fermentas.
Clasificación taxonómica de arvenses positivas para begomovirus
Las especies recolectadas e identificadas positivas fueron identificadas taxonómicamente como Sida acuta, Rivina humilis, Acalypha sp., Phaseolus vulgaris, Parthenium hysterophorus, Euphorbia hirta, Rhynchosia minima y E. heterophyla (Tabla 2). Para dos arvenses no fue posible realizar la identificación de especie debido a la ausencia de frutos y flores.
Arvenses hospederas de begomovirus
La detección de begomovirus por PCR en las arvenses recolectadas, permitió conocer nuevas familias como hospederas y ratificar aquellas previamente descritas. El grupo de investigación IPMA (Interacción-Planta-Microorganismo-Ambiente) perteneciente a la universidad Nacional de Colombia sede Palmira, previamente había descrito la presencia begomoviral en las arvenses: Momordica charantia, R. humilis, Laportea aestuans, Amaranthus dubius, Lantana cámara, Malvastrum sp., Desmodium sp., E. hirta, E. heterophyla, Parthenium hysterophorus y Croton hirtus previamente recolectadas en Palmira, Florida, Ginebra, Cerrito y Candelaria, Valle (López-López et al., 2014; Vaca-Vaca et al., 2018).
En la presente investigación fueron identificados dos nuevos hospederos alternativos para begomovirus en Colombia, los cuales fueron recolectados en Zarzal (Figura 2). Se trata de S. acuta que fue reportado como un nuevo hospedero para Colombia y Acalypha sp. que se reporta por primera vez como un nuevo hospedero para América Latina y el Caribe, resaltando así la importancia de la distribución geográfica y la alta diversidad de hospederos alternos de begomovirus. No obstante, no se sabe con certeza, si: (1) los begomovirus en Colombia se encontraban de forma latente en las arvenses, (2) con la llegada de B. tabaci migraron a plantas cultivadas, (3) ocurrió el fenómeno contrario.

Figura 2 Nuevas arvenses como hospederos alternativos de begomovirus presentes en Zarzal, Valle del Cauca (Colombia). A, Sida acuta (Z2); B, Acalypha sp. (Z19).
Estos resultados confirman que en el cultivo de ají en el Valle del Cauca (Colombia) las arvenses son un importante hospedero viral silvestre, ya que su vector principal, la mosca blanca, puede migrar de ellas a ciertos cultivares, convirtiéndose de esta forma en uno de los principales devastadores de cultivos de importancia económica (Jabloñska-Sabuka, Kalaria, y Kauranne, 2015).
Conclusiones
En un total de 179 arvenses recolectadas en sitios próximos a cultivos de ají en los municipios de Zarzal, Vijes, Toro, Unión, Roldanillo y Guacarí (Valle del Cauca, Colombia) se encontraron como positivas para hospederos alternativos de begomovirus las especies: Sida acuta, Malvastrum sp, Rivina humilis, Acalypha sp, Parthenium hysterophorus, Euphorbia hirta, Rhynchosia minima, Rhynchosia minima. Sida acuta constituye el primer reporte en Colombia como arvense hospedera de begomovirus. Para la arvense Acalypha sp. este es el primer reporte en América Latina.
La identificación de nuevos hospederos alternativos de begomovirus es una alternativa para la toma de acciones correctivas tendientes a la eliminación de arvenses hospederas de este virus, como método efectivo de control contra la diseminación de este género de la familia gemiviridae.















